Introduction
Les arbres sur cette page représente la phylogénie des haplogroupes du chromosome Y (Y-ADN) européens et moyen-orientaux. Un haplogroupe Y-ADN est un groupe d'hommes partageant la même série de mutations sur leur chromosome Y, dont ils ont hérité d'une longue lignée d'ancêtres patrilinéaires. Quelques nouvelles mutations, appellées SNP, se produisent à chaque génération et sont passées inchangées à la prochaine génération. Classer les SNP accumulées par génération permettent de retracer l'arbre généalogique de l'humanité avec une grande précision, de détecter des motifs dans la répartition des lignées historiques communes, et de retracer les migrations historiques des lignées paternelles.
La plupart des haplogroupes de niveau supérieur (p. ex. E1b1b, I1, J2, R1b) ont été formé il y a des dizaines de milliers d'années, généralement en remontant à la période Mésolithique ou Paléolithique. Les clades principales au sein d'un haplogroupe correspondent souvent à de grands groupes ethnico-linguistiques, qui sont en général indiquées avec le SNP définissant la clade en question (p. ex., E-V13, G2a-L497, J1-P58, M458-R1a, R1b-U106). Ces clades principales ont été formés dans la plupart des cas au cours du Néolithique ou de l'âge du bronze. Les clades profondes, également renseignées par le SNP les définissant (p. ex. I1-L1302, I2a2a-Z78, J1-ZS227, M2783-N1c, R1b-M222), représentent des lignées plus jeunes, qui sont apparues au cours de l'âge du fer, du moyen âge ou plus tard. Plus une sous-clade est profonde dans l'arbre phylogénétique, plus le dernier ancêtre commun parilinéaire est récent (=> voir également Comment retracer notre ascendance avec ADN ?). Le classement des SNP dans un ordre généalogique est connue sous le nom de phylogénie.
Notez que quelques SNP ont plus d'une appellation, que l'on appelle des alias (par exemple S21 et M405 sont la même mutation que U106) car les sociétés de test d'ADN qui les ont découverts possède chacun leur propre nomenclature. Par exemple, les SNP qui commencent par M ont été identifiés par l'Université de Stanford en Californie, ceux de la série L (p. ex. L21) ont été trouvés par la société Family Tree DNA au Texas, les PF par l'Université de Sassari en Italie, les U (p. ex. U152) de l'Université de Floride centrale, les S (p. ex. S21) par la société EthnoAncestry, et le CTS par le Welcome Trust Sanger Institute à Cambridge au Royaume-Uni. Les séries DF et Z proviennent de divers membres de la communauté de généalogie génétique, tandis que la série Y a été identifiée par Yfull.com.
Les tests Y-ADN ont existé depuis le début des années 2000, mais les tests étaient à l'époque limité aux SNP individuels (un seul à la fois). Puis, d'année en année, vinrent des lots de dizaines, puis de centaines, puis de milliers de SNP. Depuis 2014, les nouveaux tests commerciaux permettent le séquençage de millions de SNP à la fois, couvrant la majeure partie du chromosome Y. Ceci a permis la découverte rapide de dizaines de milliers de nouveaux SNP, ce qui permis d'établir des arbres phylogénétiques à une très haute résolution, avec parfois seulement quelques générations séparant les ramifications les plus profondes de l'arbre. Il serait encombrant d'afficher une telle résolution ici, et pour cette raison nous avons décidé de limiter la profondeur jusqu'au Moyen Âge, lorsque sont se formés les groupes ethniques modernes. Le pionnier du séquençage du chromosome Y entier a été Full Genome Corpration et les SNP découvert par cette compagnie commencent par FGC. Family Tree DNA a mis au point un test similaire, appelé Big Y, dont les SNP sont représentés par BY (=> voir également Quel test ADN choisir ?).
Il est important de savoir que beaucoup d'haplogroupes et de clades sont définies par plus qu'un SNP. Les lignées paléolithiques qui ont subi des goulots d'étranglement de population importants pendant des milliers d'années, ont parfois une série de plus d'une centaine de SNP les définissant (p. ex. les haplogroupes G et I1 sont chacun définis par plus de 300 SNP). De manière générale, le nombre accumulé de SNP entre un chromosome Y et sa sous-clade directe corrèle plus ou moins avec le nombre de générations écoulées. (C'est un peu plus compliqué que cela, comme des mutations se produisent plus fréquemment sur certains segments du chromosome Y que sur des autres, et ce facteur devrait aussi être pris en compte pour l'estimation de l'âge d'une clade.) Cette page vise à fournir des arbres qui sont faciles à visualiser et par conséquent seulement le SNP les plus couramment utilisé sera indiqué. Parfois un alias sera montré, si les deux sont utilisés régulièrement. Dans ce cas, les deux SNP équivalents seront séparés par une barre oblique (par exemple U106/S21). Pour une liste exhaustive des mutations, veuillez consulter Yfull.com (qui inclut également l'estimation de l'âge et le TMRCA pour la plupart sous-clades) ou The Big Tree (encore plus détaillé, mais seulement disponible pour les clades de R1b-P312).
Développement chronologique des principaux haplogroupes Y-ADN d'Eurasie occidentale depuis le Paléolithique tardif jusqu'à l'âge du fer
Arbre phylogénétique de l'haplogroupe E1b1b

Arbre phylogénétique de l'haplogroupe E-V13
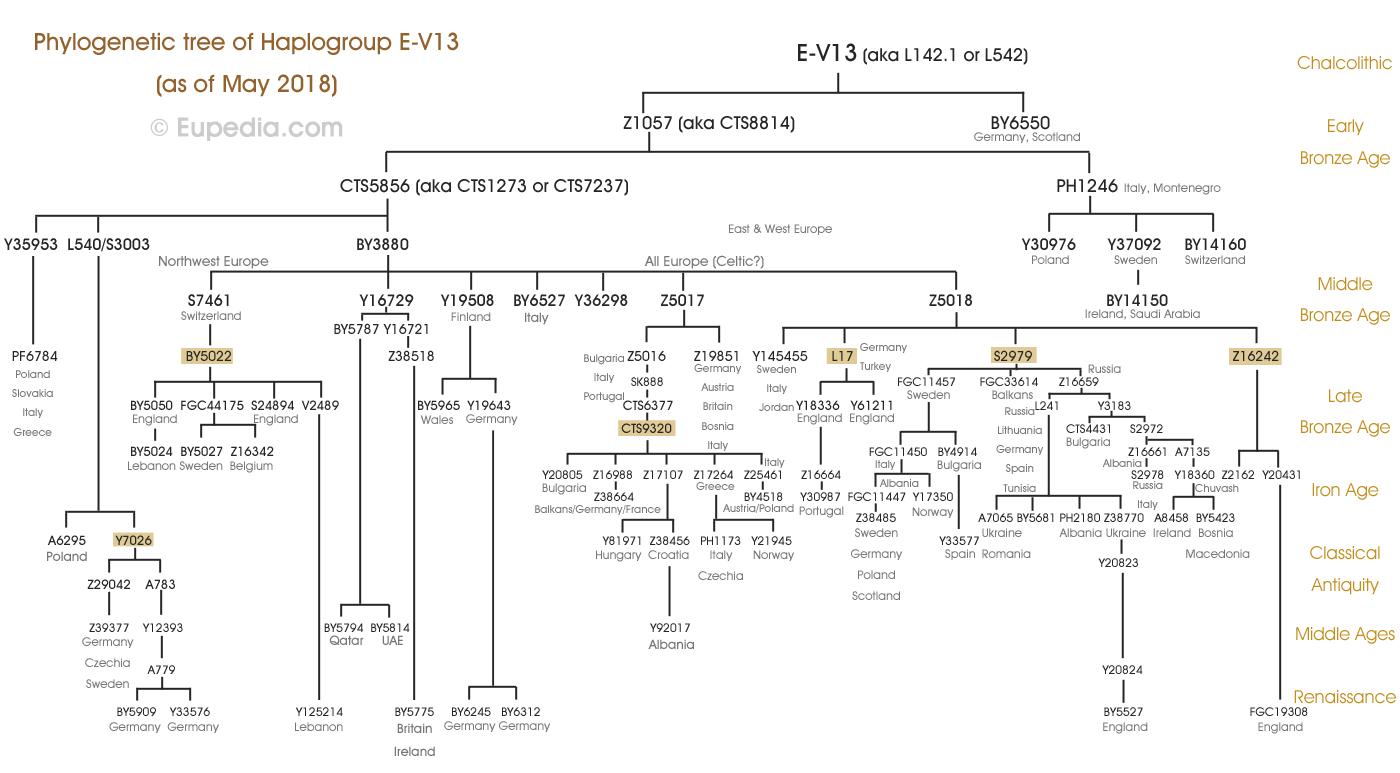
Arbre phylogénétique de l'haplogroupe E-M123
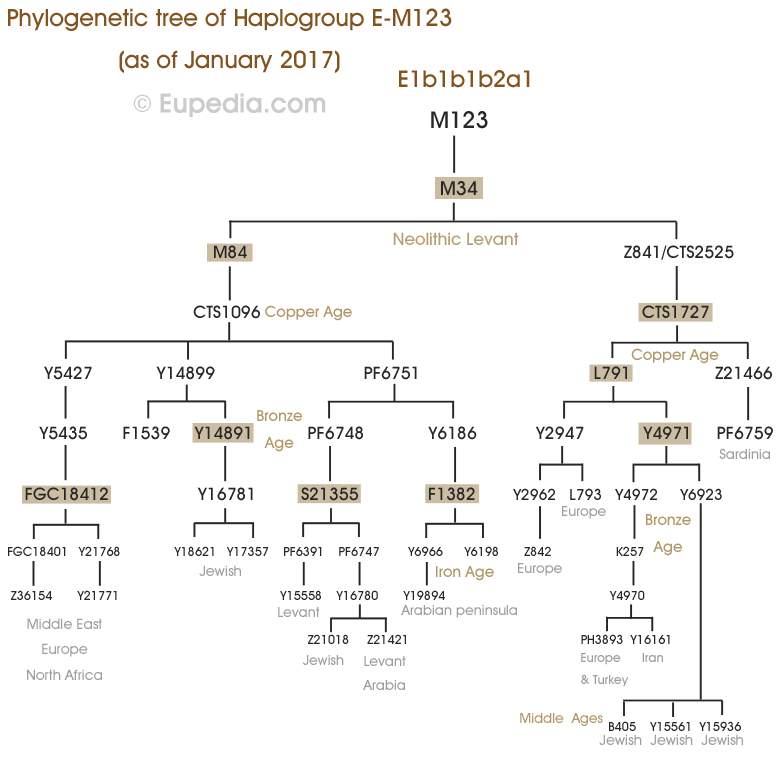
Arbre phylogénétique de l'haplogroupe G2a
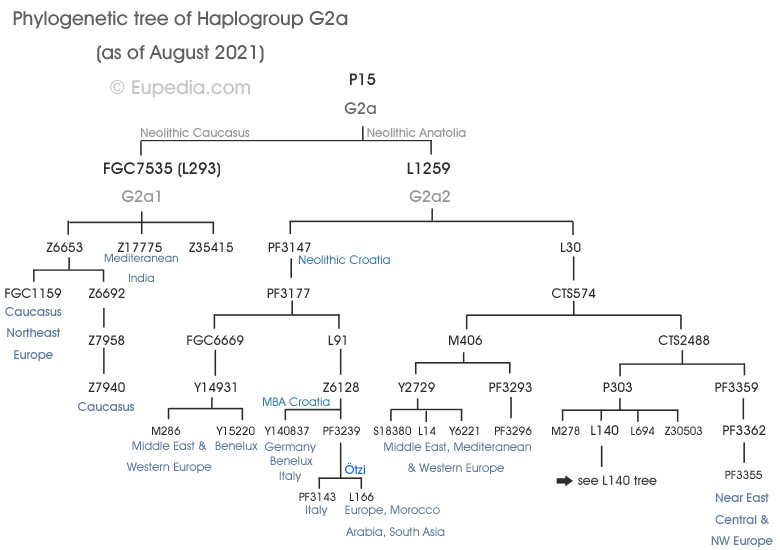
Arbre phylogénétique de l'haplogroupe G2a-L140
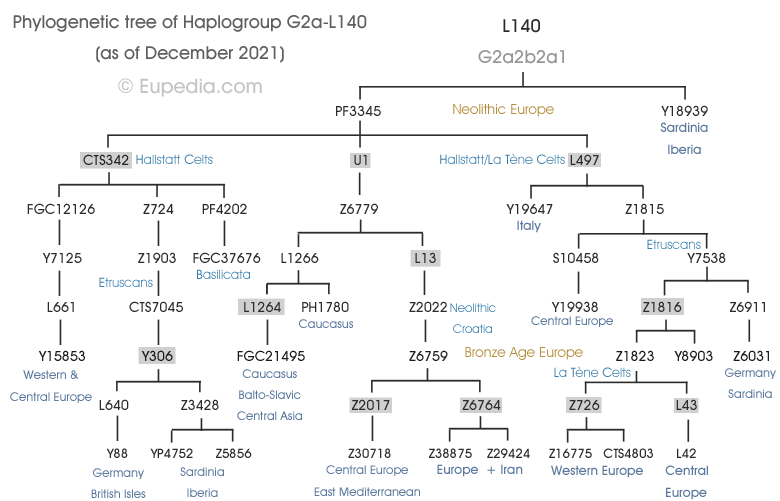
Arbre phylogénétique de l'haplogroupe I1
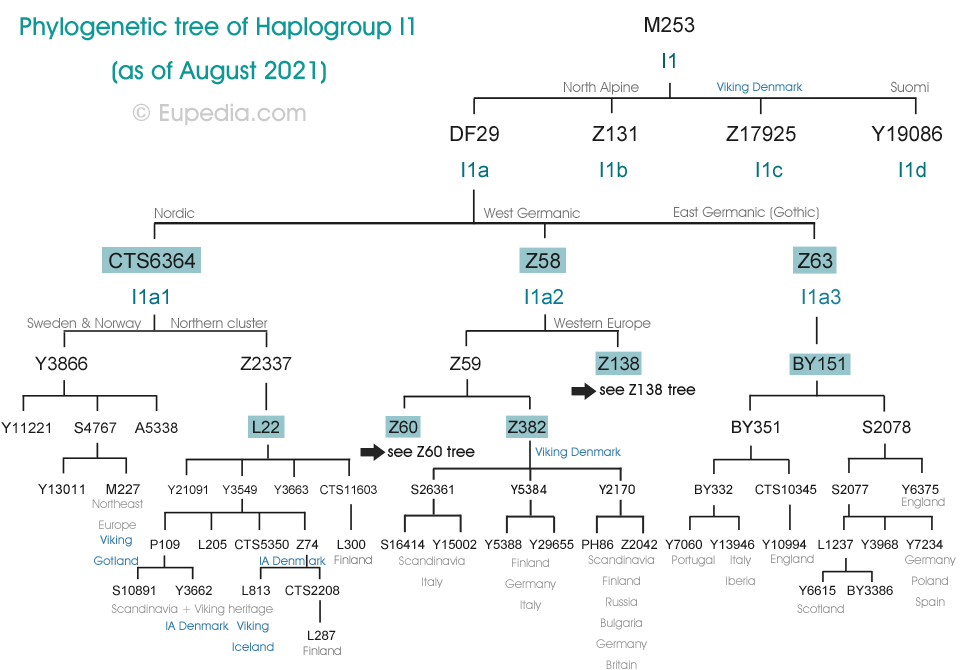
Arbre phylogénétique de l'haplogroupe I1-L22

Arbre phylogénétique de l'haplogroupe I1-Z74

Arbre phylogénétique de l'haplogroupe I1-S14887

Arbre phylogénétique de l'haplogroupe I1-Z60

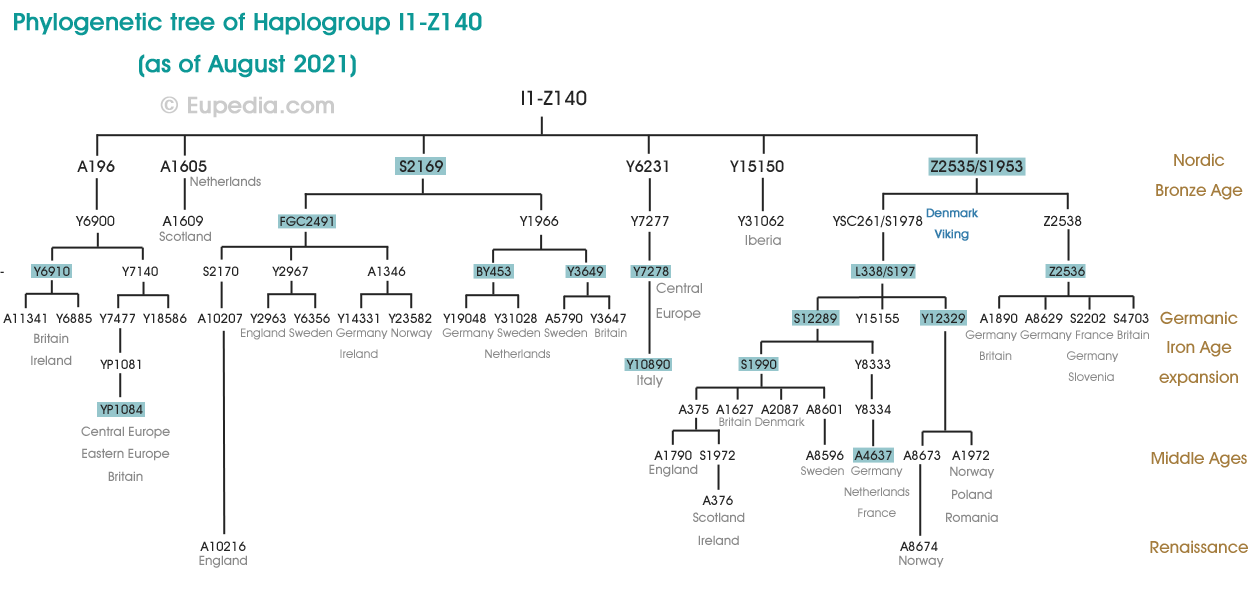
Arbre phylogénétique de l'haplogroupe I1-Z140
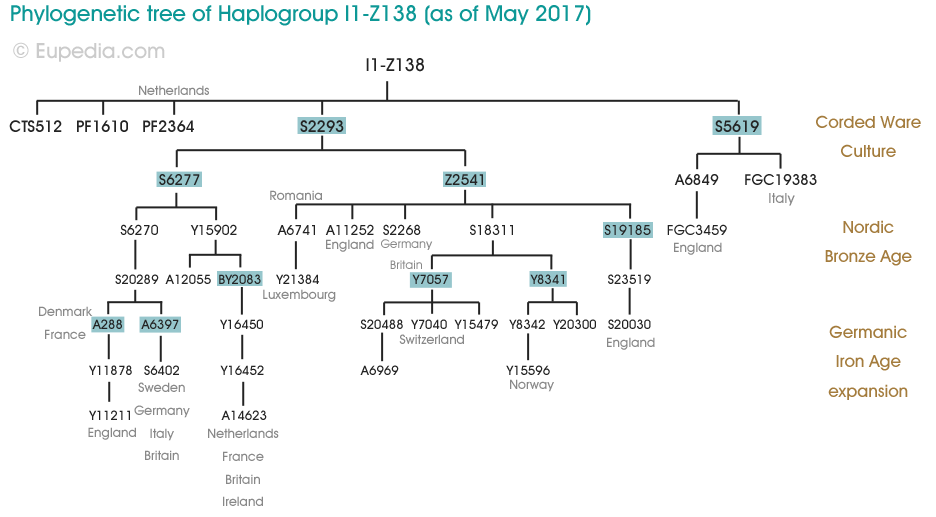
Arbre phylogénétique de l'haplogroupe I1-Z138

Arbre phylogénétique de l'haplogroupe I2

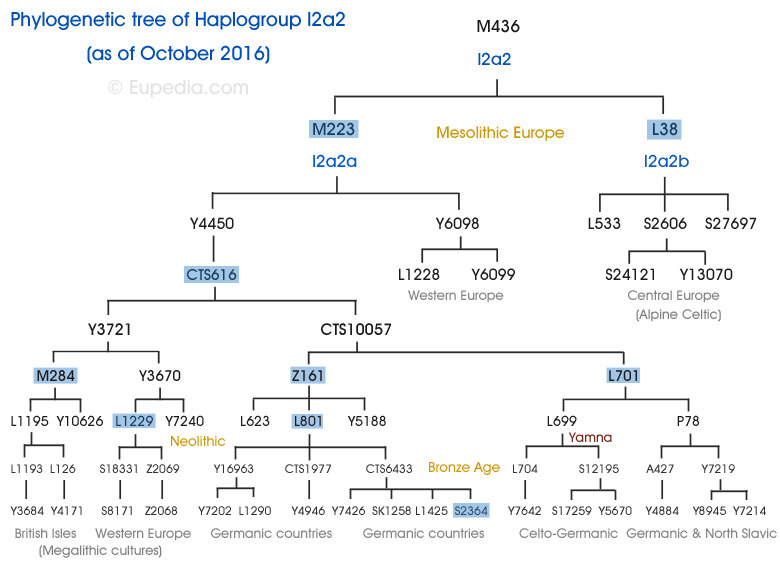
Arbre phylogénétique de l'haplogroupe I2a2
Arbre phylogénétique de l'haplogroupe I2a2-L801
Click to enlarge

Arbre phylogénétique de l'haplogroupe J1

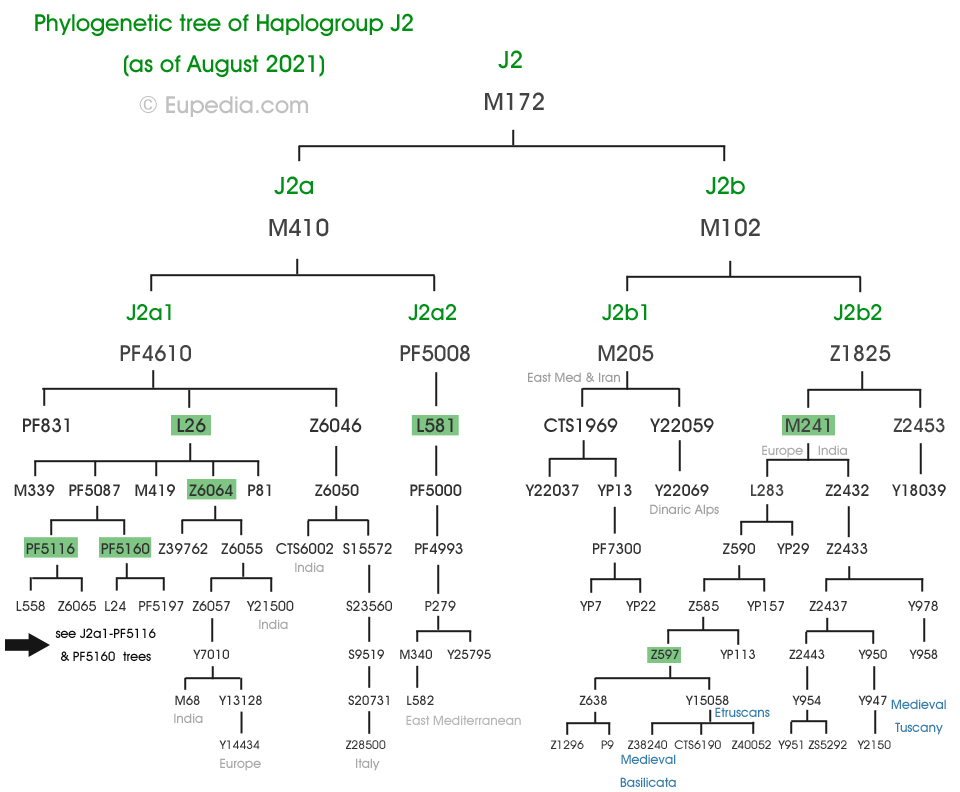
Arbre phylogénétique de l'haplogroupe J2
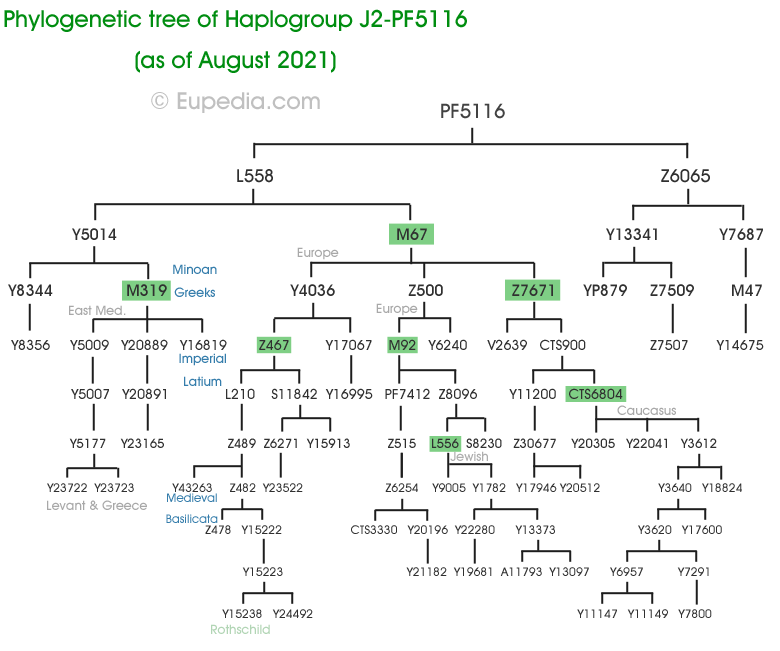
Arbre phylogénétique de l'haplogroupe J2-PF5116
Arbre phylogénétique de l'haplogroupe J2-PF5160

Arbre phylogénétique de l'haplogroupe N1c
Click to enlarge

Arbre phylogénétique de l'haplogroupe Q1a
Click to enlarge

Arbre phylogénétique de l'haplogroupe Q1b
Click to enlarge

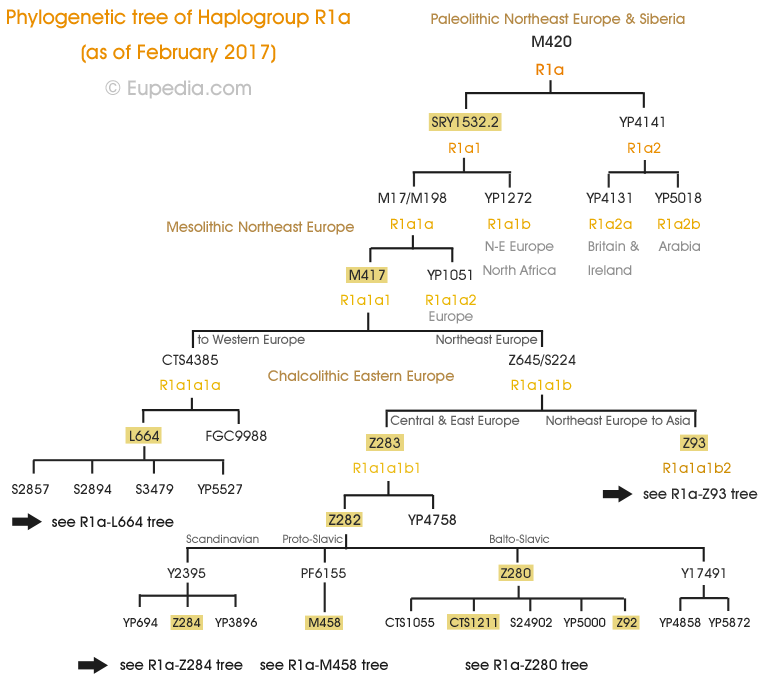
Arbre phylogénétique de l'haplogroupe R1a
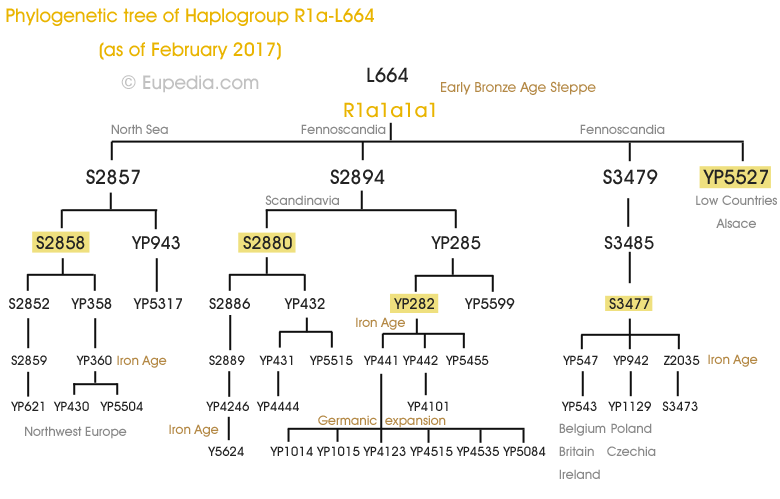
Arbre phylogénétique de l'haplogroupe R1a-L664
Arbre phylogénétique de l'haplogroupe R1a-Z284
Click to enlarge

Arbre phylogénétique de l'haplogroupe R1a-M458
Click to enlarge

Arbre phylogénétique de l'haplogroupe R1a-Z280
Click to enlarge

Arbre phylogénétique de l'haplogroupe R1a-Z93
Click to enlarge

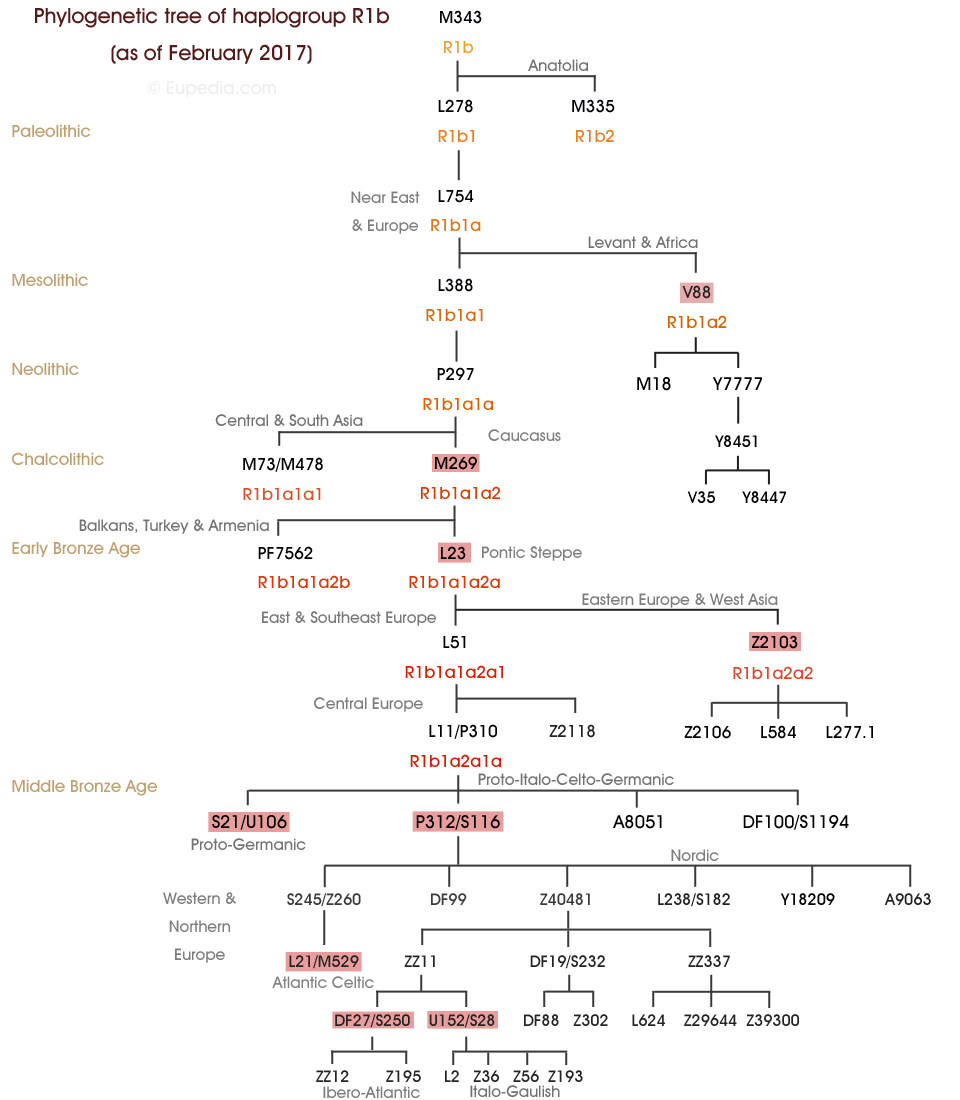
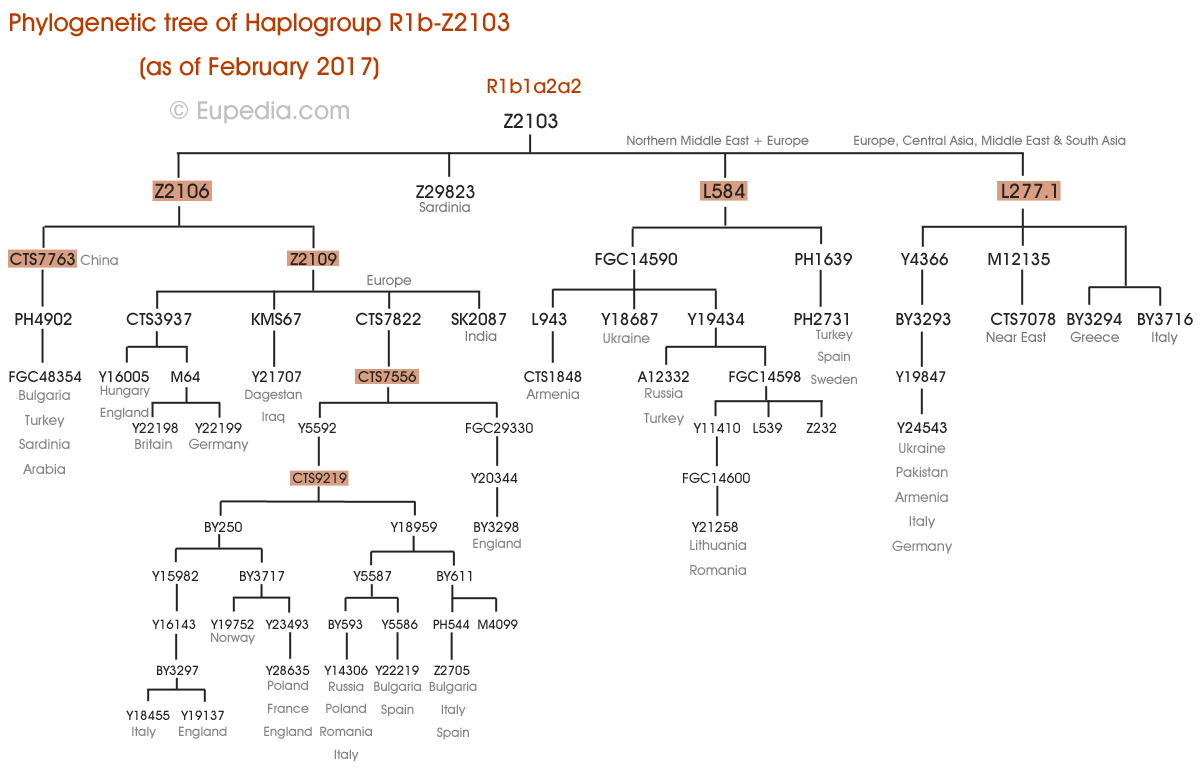
Arbre phylogénétique de l'haplogroupe R1b-Z2103
Click to enlarge
Arbre phylogénétique de l'haplogroupe R1b-U106 (aka S21 or M405)
Click to enlarge

Arbre phylogénétique de l'haplogroupe R1b-Z381
Click to enlarge

Arbre phylogénétique de l'haplogroupe R1b-U152 (aka S28 or PF6570)
Click to enlarge

Arbre phylogénétique de l'haplogroupe R1b-L2
Click to enlarge

Arbre phylogénétique de l'haplogroupe R1b-ZZ12
Click to enlarge

Arbre phylogénétique de l'haplogroupe R1b-Z195
Click to enlarge

Arbre phylogénétique de l'haplogroupe R1b-L21 (aka S145 or M529)
Click to enlarge

Arbre phylogénétique de l'haplogroupe R1b-Z39589
Click to enlarge

Arbre phylogénétique de l'haplogroupe T

Arbre phylogénétique de l'haplogroupe T1a-CTS2214

Follow-up
